|
|
 发表于 昨天 20:48
|
发表于 昨天 20:48
|
查看: 3 |
回复: 0
原文献:Cell, 2025, 188, 6939–6952.
参考基因组的选择会显著影响群体基因组学的分析结果
作者:Maria Akopyan, Matthew Genchev, Ellie E. Armstrong, Jazlyn A. Mooney
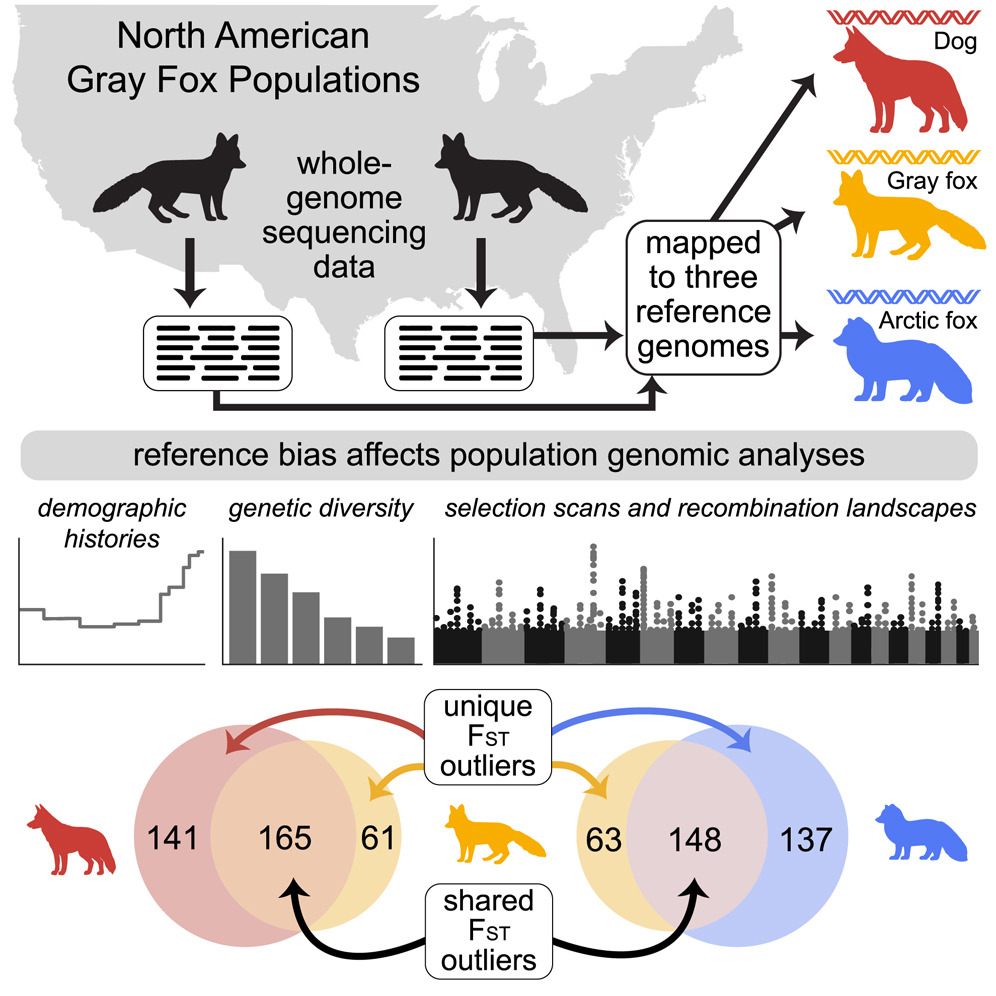
南加州大学Jazlyn A. Mooney课题组的一项发表在Cell期刊上的研究指出,参考基因组的选择会显著影响群体基因组学的分析结果。课题组通过将灰狐(Urocyon cinereoargenteus)的全基因组测序数据分别比对至同种参考基因组以及两种异种犬科动物(家犬和北极狐)的基因组,证实了“参考偏差”会显著影响群体基因组学的分析结果。与比对至异种基因组相比,比对至同种基因组显著提高了测序读段的配对率(提升幅度约为5%),并能够检测出多达26%–32%的额外单核苷酸多态性位点(SNPs)以及 33%–35% 的额外单例变异。采用同种参考基因组后,核苷酸多样性的估算值提升了超过 30%,群体分化指数(FST)从0.189上升至0.197,而有效群体大小的估算值也随之提高了30%–60%。此外,若采用异种参考基因组,染色体两端的重组率估算值甚至会出现高达 3 倍的差异。尤为重要的是,FST 离群值的检测结果呈现出显著差异:采用异种基因组进行分析时,所识别出的独特离群窗口数量竟是采用同种基因组时的两倍。参考偏差会导致对遗传多样性及群体分化程度的低估。上述研究结果不仅突显了参考基因组选择对分析结果的影响,更强调了拥有同种基因组资源对于开展准确的演化推断具有不可或缺的重要性。
文章核心要点:
- 物种特异性的参考基因组能够提升测序读段的比对效率及变异检测的准确性
- 亲缘关系较远的参考基因组会扭曲对群体历史动态及重组图景的解析
- 采用不同的参考基因组会检测出各异的FST离群值,进而影响对相关基因功能进行解读的准确性
附原文献链接(百度网盘):
|
|